Conformers:
ABBIImiBZICOPNSYNN
Click the Summary/Torsions/Similar/... tabs for more details.
Holliday Junctions formed from Telomeric DNA
Click a row in table or a step in viewer for analysis of results. Click column headers to sort data.
Steps with non-standard or missing atoms have not been assigned, description of conformers is defined in the table.
Results of the assignment of 82 detected steps in 1 model(s), can be also downloaded as csv or json file. Average confal 0, percentile 0.
Click a row in table or a step in viewer for analysis of results. Click column headers to sort data.
Define restraints for steps within Å cartesian RMSD, global sigma scaling factor or use per step sigma scaling.
| step number | Step name | CANA | NtC | confal | rmsd |
|---|---|---|---|---|---|
| 01 | 6gdn_A_DG1_DG2 | A-B | AB01 | 69 | 0.22 |
| 02 | 6gdn_A_DG2_DT3 | BBB | BB00 | 82 | 0.23 |
| 03 | 6gdn_A_DT3_DT4 | BBB | BB00 | 58 | 0.17 |
| 04 | 6gdn_A_DT4_DA5 | NAN | NANT | 0 | 0.52 |
| 05 | 6gdn_A_DA5_DG6 | B-A | BA17 | 57 | 0.36 |
| 06 | 6gdn_A_DG6_DG7 | miB | BB14 | 8 | 0.40 |
| 07 | 6gdn_A_DG7_DG8 | BBB | BB00 | 19 | 0.23 |
| 08 | 6gdn_A_DG8_DT9 | BBB | BB01 | 40 | 0.22 |
| 09 | 6gdn_A_DT9_DT10 | BBB | BB00 | 24 | 0.19 |
| 10 | 6gdn_A_DT10_DC11 | BBB | BB00 | 51 | 0.39 |
| 11 | 6gdn_A_DC11_DT12 | NAN | NANT | 0 | 0.94 |
| 12 | 6gdn_A_DT12_DT13 | NAN | NANT | 0 | 1.19 |
| 13 | 6gdn_A_DT13_DG14 | NAN | NANT | 0 | 0.76 |
| 14 | 6gdn_A_DG14_DA15 | BBB | BB00 | 70 | 0.25 |
| 15 | 6gdn_A_DA15_DA16 | BBB | BB00 | 91 | 0.15 |
| 16 | 6gdn_A_DA16_DC17 | OPN | OP11 | 27 | 0.58 |
| 17 | 6gdn_A_DC17_DC18 | AAA | AA00 | 35 | 0.26 |
| 18 | 6gdn_A_DC18_DC19 | A-B | AB01 | 21 | 0.31 |
| 19 | 6gdn_A_DC19_DT20 | NAN | NANT | 0 | 0.80 |
| 20 | 6gdn_A_DT20_DT21 | NAN | NANT | 0 | 0.99 |
| 21 | 6gdn_A_DT21_DG22 | NAN | NANT | 0 | 1.85 |
| 22 | 6gdn_A_DG22_DG23 | NAN | NANT | 0 | 2.05 |
| 23 | 6gdn_A_DG23_DG24 | AAw | AA10 | 73 | 0.37 |
| 24 | 6gdn_A_DG24_DT25 | NAN | NANT | 0 | 0.53 |
| 25 | 6gdn_A_DT25_DT26 | NAN | NANT | 0 | 0.54 |
| 26 | 6gdn_A_DT26_DA27 | miB | BB10 | 74 | 0.20 |
| 27 | 6gdn_A_DA27_DC28 | BBw | BB11 | 55 | 0.45 |
| 28 | 6gdn_A_DC28_DT29 | NAN | NANT | 0 | 1.31 |
| 29 | 6gdn_A_DT29_DT30 | NAN | NANT | 0 | 2.07 |
| 30 | 6gdn_A_DT30_DG31 | NAN | NANT | 0 | 1.68 |
| 31 | 6gdn_A_DG31_DT32 | NAN | NANT | 0 | 0.42 |
| 32 | 6gdn_A_DT32_DA33 | NAN | NANT | 0 | 0.45 |
| 33 | 6gdn_A_DA33_DA34 | NAN | NANT | 0 | 0.48 |
| 34 | 6gdn_A_DA34_DC35 | NAN | NANT | 0 | 0.53 |
| 35 | 6gdn_A_DC35_DC36 | A-B | AB04 | 42 | 0.34 |
| 36 | 6gdn_A_DC36_DC37 | BBB | BB01 | 51 | 0.21 |
| 37 | 6gdn_A_DC37_DT38 | A-B | AB03 | 43 | 0.46 |
| 38 | 6gdn_A_DT38_DA39 | NAN | NANT | 0 | 0.83 |
| 39 | 6gdn_A_DA39_DA40 | BBw | BB02 | 66 | 0.30 |
| 40 | 6gdn_A_DA40_DC41 | NAN | NANT | 0 | 0.41 |
| 41 | 6gdn_A_DC41_DC42 | NAN | NANT | 0 | 0.64 |
| 42 | 6gdn_B_DG1_DG2 | NAN | NANT | 0 | 0.45 |
| 43 | 6gdn_B_DG2_DT3 | NAN | NANT | 0 | 0.46 |
| 44 | 6gdn_B_DT3_DT4 | NAN | NANT | 0 | 0.46 |
| 45 | 6gdn_B_DT4_DA5 | B12 | BB04 | 46 | 0.25 |
| 46 | 6gdn_B_DA5_DG6 | B-A | BA10 | 44 | 0.46 |
| 47 | 6gdn_B_DG6_DG7 | AAw | AA11 | 44 | 0.43 |
| 48 | 6gdn_B_DG7_DG8 | A-B | AB04 | 28 | 0.44 |
| 49 | 6gdn_B_DG8_DT9 | NAN | NANT | 0 | 0.45 |
| 50 | 6gdn_B_DT9_DT10 | NAN | NANT | 0 | 0.40 |
| 51 | 6gdn_B_DT10_DC11 | AAA | AA02 | 19 | 0.58 |
| 52 | 6gdn_B_DC11_DT12 | NAN | NANT | 0 | 0.80 |
| 53 | 6gdn_B_DT12_DT13 | NAN | NANT | 0 | 0.46 |
| 54 | 6gdn_B_DT13_DG14 | NAN | NANT | 0 | 0.49 |
| 55 | 6gdn_B_DG14_DA15 | BBB | BB00 | 82 | 0.28 |
| 56 | 6gdn_B_DA15_DA16 | BBB | BB00 | 83 | 0.20 |
| 57 | 6gdn_B_DA16_DC17 | OPN | OP11 | 35 | 0.69 |
| 58 | 6gdn_B_DC17_DC18 | A-B | AB04 | 52 | 0.28 |
| 59 | 6gdn_B_DC18_DC19 | NAN | NANT | 0 | 0.43 |
| 60 | 6gdn_B_DC19_DT20 | NAN | NANT | 0 | 0.76 |
| 61 | 6gdn_B_DT20_DT21 | NAN | NANT | 0 | 1.47 |
| 62 | 6gdn_B_DT21_DG22 | NAN | NANT | 0 | 1.41 |
| 63 | 6gdn_B_DG22_DG23 | NAN | NANT | 0 | 2.16 |
| 64 | 6gdn_B_DG23_DG24 | NAN | NANT | 0 | 0.65 |
| 65 | 6gdn_B_DG24_DT25 | NAN | NANT | 0 | 0.49 |
| 66 | 6gdn_B_DT25_DT26 | miB | BB15 | 61 | 0.33 |
| 67 | 6gdn_B_DT26_DA27 | B-A | BA05 | 54 | 0.32 |
| 68 | 6gdn_B_DA27_DC28 | A-B | AB01 | 12 | 0.44 |
| 69 | 6gdn_B_DC28_DT29 | NAN | NANT | 0 | 0.69 |
| 70 | 6gdn_B_DT29_DT30 | NAN | NANT | 0 | 1.82 |
| 71 | 6gdn_B_DT30_DG31 | NAN | NANT | 0 | 1.03 |
| 72 | 6gdn_B_DG31_DT32 | NAN | NANT | 0 | 0.75 |
| 73 | 6gdn_B_DT32_DA33 | BB2 | BB07 | 65 | 0.27 |
| 74 | 6gdn_B_DA33_DA34 | BBB | BB00 | 62 | 0.27 |
| 75 | 6gdn_B_DA34_DC35 | OPN | OP11 | 41 | 0.60 |
| 76 | 6gdn_B_DC35_DC36 | AAA | AA00 | 73 | 0.29 |
| 77 | 6gdn_B_DC36_DC37 | AAA | AA00 | 21 | 0.41 |
| 78 | 6gdn_B_DC37_DT38 | A-B | AB01 | 35 | 0.38 |
| 79 | 6gdn_B_DT38_DA39 | NAN | NANT | 0 | 0.94 |
| 80 | 6gdn_B_DA39_DA40 | NAN | NANT | 0 | 0.63 |
| 81 | 6gdn_B_DA40_DC41 | B-A | BA01 | 26 | 0.40 |
| 82 | 6gdn_B_DC41_DC42 | AAA | AA04 | 63 | 0.43 |
Steps with non-standard or missing atoms have not been assigned, description of conformers is defined in the table.
|
step: Table of conformers |
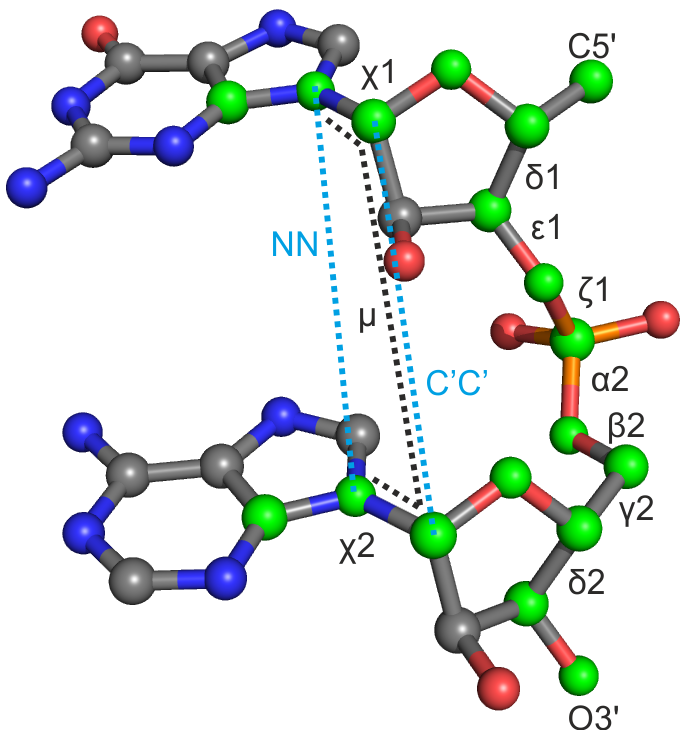
| δ1 | ε1 | ζ1 | α2 | β2 | γ2 | δ2 | χ1 | χ2 | μ | NN | CC | |
| step_torsions | ||||||||||||
| ntC_average | ||||||||||||
| Δ torsions | ||||||||||||
| torsion scores |
| comments | step confal = NaN cartesian RMSD = NaN Å pseudorotation: NA details: NA |
Similarity of step to class averages
Download
Results as csv or json file.Best NtC fitted to input structure.
Restraints
Restraints file for REFMAC (steps with RMSD <= 0.5Å)Commands file for MMB (steps with RMSD <= 0.5Å)
Restraints file for Phenix (steps with RMSD <= 0.5Å) [?]
Definitions
Average parameters (csv), esd values (csv), and Cartesian coordinates of conformers.Download the papers
Description of DNATCO server:Černý et al., Nucleic Acids Research, 44, W284 (2016).
Definition of conformers:
Schneider et al., Acta Cryst D, 74, 52-64 (2018).
Example of application:
Schneider et al., Genes, 8(10), 278, (2017).
Browse conformers
Show
| Color by conformation group (pyramids) | |
|---|---|
| group | |||||||||
| visible |
| Color by NtC (balls) |
|---|
| A | ||||
|---|---|---|---|---|
| A-B | ||||
|---|---|---|---|---|
| B-A | ||||
|---|---|---|---|---|
| B | ||||
|---|---|---|---|---|
| IC | ||||
|---|---|---|---|---|
| OPN | ||||
|---|---|---|---|---|
| Z | ||||
|---|---|---|---|---|
| N | ||||
|---|---|---|---|---|